序列比对是基因组研究和临床诊断的基础起点,是将原始测序数据转化为有意义生物学见解的关键桥梁 。准确的比对直接影响变异检测、基因组组装和个性化智慧医疗等下游分析的质量 。
2026年1月,朱山风团队在《Nature Communications》上发表了题为VACmap: An Accurate Long-Read Aligner for Unraveling Complex Genomic Rearrangements的研究论文。
朱山风团队提出了一种基于非线性比对的长读段比对算法 VACmap 。VACmap克服了传统线性比对算法在处理复杂重排时的局限。不同于传统方法将读段拆分并依赖后期筛选冗余子比对的模式,VACmap提出了一种基于加权有向无环图(DAG)的非线性比对新范式 。该算法将整条长读长序列视为一个不可分割的统一实体,通过 K-mer 匹配构建图结构,并将 K-mer 匹配间的连接分类为“正常边”与“变异边” 。通过在 DAG 图中搜索加权最长路径,VACmap 能够在不拆分读段的前提下,直接描绘出读段在参考基因组上的真实游走轨迹,从而无需拆分读段即可精准捕捉并还原复杂的基因组结构变异事件。
在医学相关基因(CMRG)基准测试中,VACmap 展现了显著优于当前线性比对工具的性能。特别是在难以检测的重复变异类别中,它将检测灵敏度从现有工具的 20%提升至 90%。这种高精度的比对能力,能直接用于解决临床实际问题,尤其是在基因组中那些序列高度相似、被称为“基因组暗物质”的区域。例如,VACmap 能够准确量化与冠心病风险高度相关的 LPA 基因中 KIV-2 重复单元的拷贝数,为心血管疾病的遗传风险评估提供依据 。针对帕金森病相关基因 GBA1 和遗传性耳聋基因 STRC,它成功识别出了被其他主流工具漏检的致病性大片段缺失,减少了临床诊断中的假阴性。此外,在 SIGLEC11/16 和 RHCE/RHD 等高度同源的基因家族中,该算法还修正了以往被误判的基因转换事件,还原了真实的遗传图谱 。
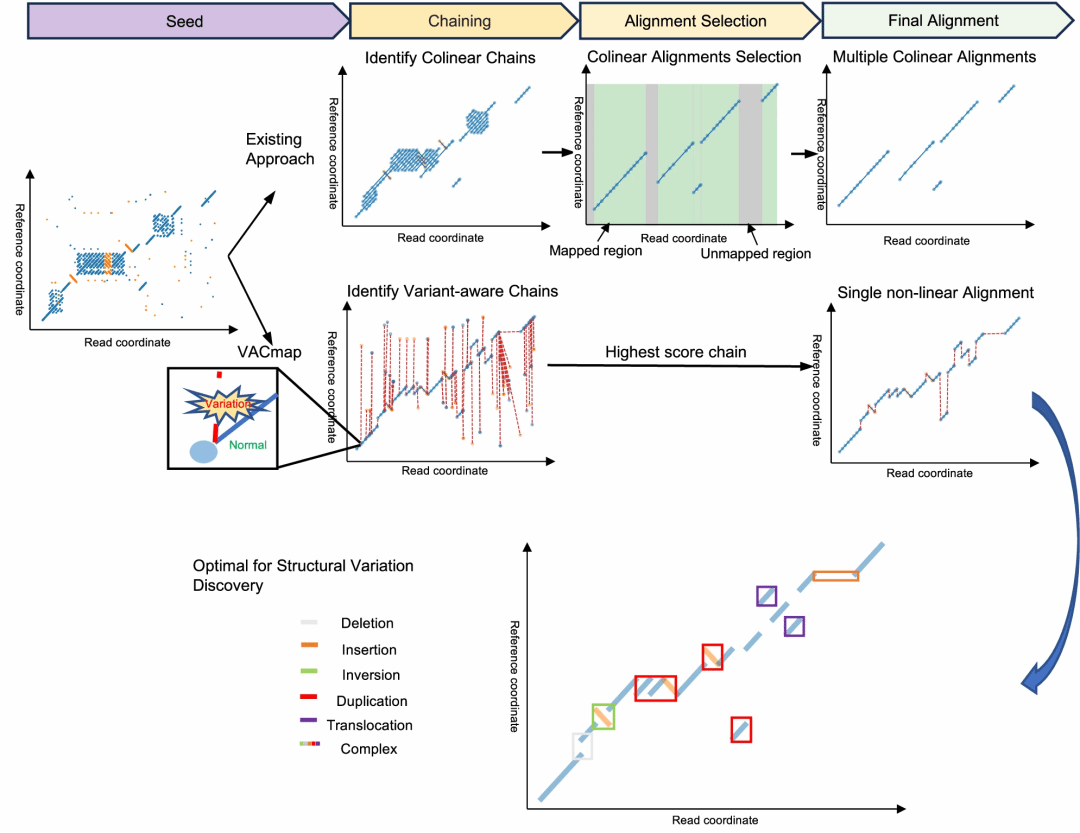
▲图1:VACmap框架
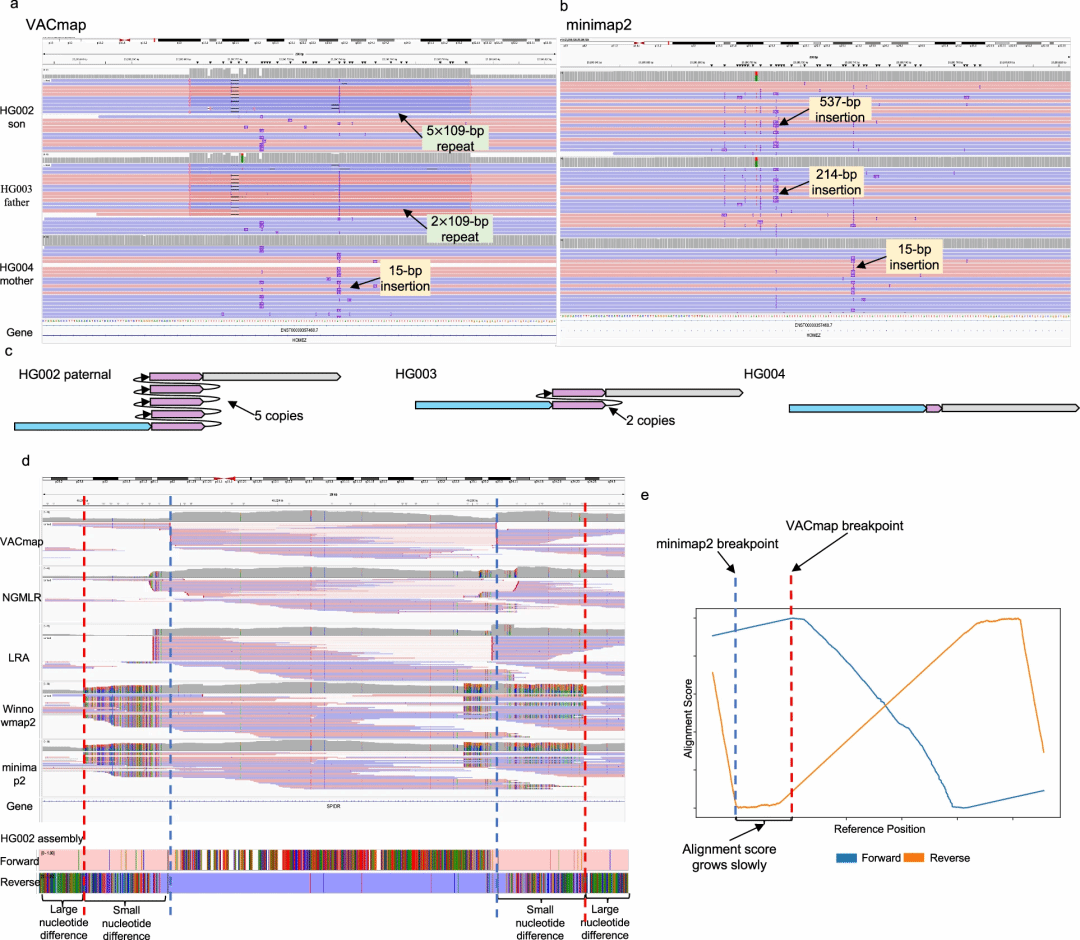
▲图2:解析GBA1/GBAP1和 STRC/STRCP1致病性缺失变异
原文链接:https://www.nature.com/articles/s41467-025-67096-7